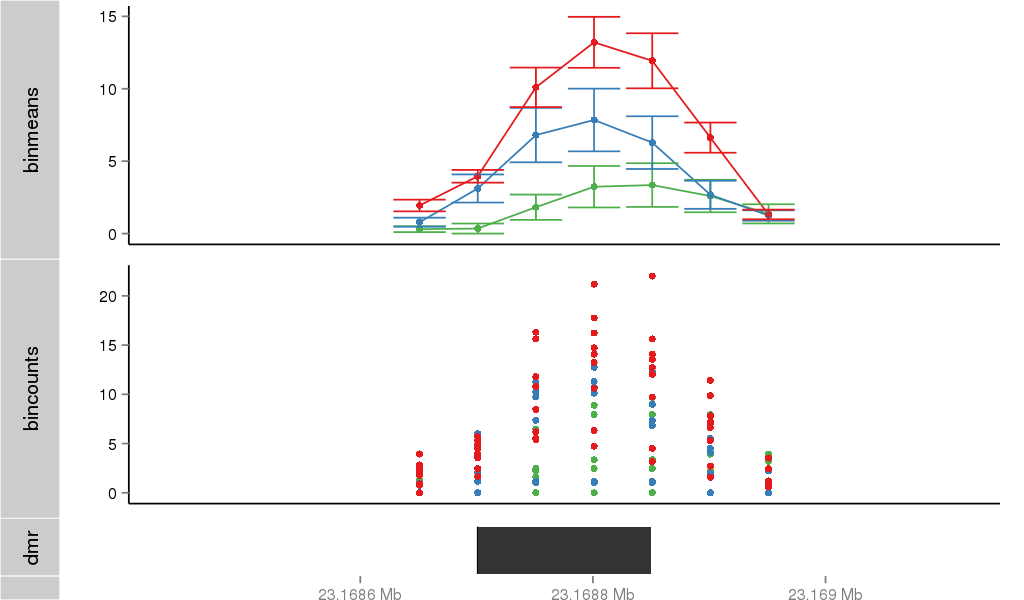
DMR 25133 chr1:23168701-23168850 (150bp)
| DMR Stats | |
|---|---|
| Position | chr1:23168701-23168850 (View on UCSC) |
| Width | 150bp |
| Genomic Context | intron |
| Nearest Genes | EPHB2 (0bp away) |
| ANODEV p-value | 0.000116189190899 |
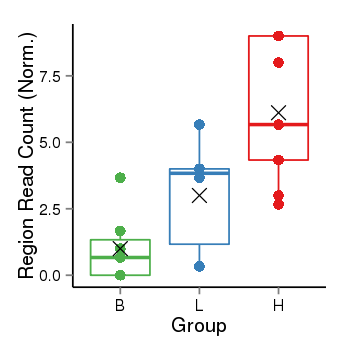
| Frequencies | Benign: 1.0 (14.29%), Low: 4.0 (66.67%), High: 7.0 (77.78 %) |
| Frequent? |
Region Count Boxplot
Region Overview
Gene Overlaps
| Dmrid | Gene Symbol | Gene Id | Isoform Id | Isoform Chr | Isoform Start | Isoform End | Isoform Strand | Overlap Bp | Query Overlap Per | Isoform Overlap Per | Noncoding | Promoter Per | Exonintron Per | End Per |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 25133 | EPHB2 | 407 | uc001bge.3 | chr1 | 23037331 | 23241823 | + | 150 | 100.0 | 0.63 | 0 | 0.0 | E1 (0), I1 (0), E2 (0), I2 (0), E3 (0), I3 (100), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (0), I8 (0), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0) | 0.0 |
| 25133 | EPHB2 | 407 | uc001bgf.3 | chr1 | 23037331 | 23241823 | + | 150 | 100.0 | 0.27 | 0 | 0.0 | E1 (0), I1 (0), E2 (0), I2 (0), E3 (0), I3 (100), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (0), I8 (0), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0) | 0.0 |
| 25133 | EPHB2 | 407 | uc009vqj.1 | chr1 | 23037331 | 23241082 | + | 150 | 100.0 | 0.27 | 0 | 0.0 | E1 (0), I1 (0), E2 (0), I2 (0), E3 (0), I3 (100), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (0), I8 (0), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0), I16 (0), E17 (0) | 0.0 |
| 25133 | EPHB2 | 407 | uc010odu.2 | chr1 | 23037332 | 23241823 | + | 150 | 100.0 | 0.36 | 0 | 0.0 | E1 (0), I1 (0), E2 (0), I2 (0), E3 (0), I3 (0), E4 (0), I4 (100), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (0), I8 (0), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0) | 0.0 |
- 4 geness
Feature Overlaps
| Dmrid | Feature Chr | Feature Start | Feature End | Set | Name | Fields |
|---|---|---|---|---|---|---|
| 25133 | chr1 | 23168586 | 23168815 | wgEncodeRegDnaseClusteredV2 | 15 | score:367, srow:18531 |
| 25133 | chr1 | 23168700 | 23168714 | tfbsConsSites | V$TST1_01 | score:846, zScore:1.98, srow:48642 |
| 25133 | chr1 | 23168701 | 23168714 | tfbsConsSites | V$CHX10_01 | score:862, zScore:2.72, srow:48643 |
| 25133 | chr1 | 23168703 | 23168715 | tfbsConsSites | V$OCT1_03 | score:888, zScore:2.05, srow:48644 |
| 25133 | chr1 | 23168687 | 23168712 | phastConsElements100way | lod=109 | score:458, srow:90742 |
| 25133 | chr1 | 23168723 | 23168729 | phastConsElements100way | lod=27 | score:320, srow:90743 |
| 25133 | chr1 | 23168754 | 23168759 | phastConsElements100way | lod=23 | score:304, srow:90744 |
- 7 featuress
Omics Overlaps
| Dmrid | Omic Set | Data | Plot |
|---|---|---|---|
| 25133 | cellmeth_recounts | PrEC: 0, LNCaP: 3, DU145: 0 | 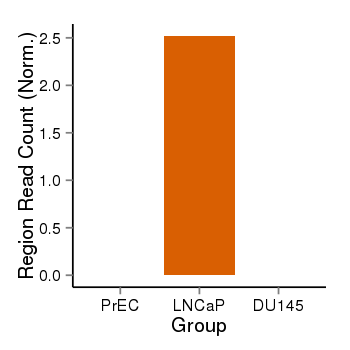 |
| 25133 | cellexp | id=ENSG00000133216, name=EPHB2, PrEC=413, str=2906, LNCaP=492, str=454, DU145=323, str=463 | 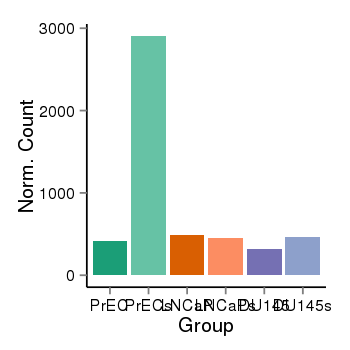 |
| 25133 | tcgaexp | gene=EPHB2, entrez=2048, pos=chr1:23037331-23241823(+), B=495, L=374, M=321, H=349 | 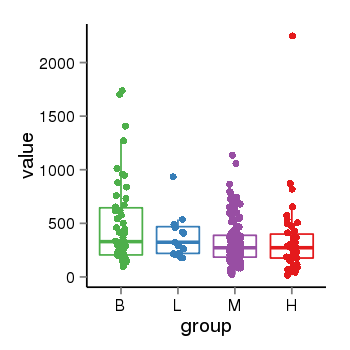 |
| 25133 | tcgaexp | gene=SRSF10, entrez=10772, pos=chr1:36273-24306953(-), B=3487, L=3388, M=3432, H=4019 | 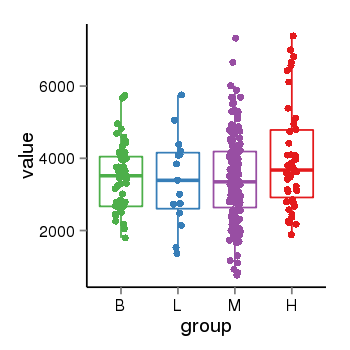 |
| 25133 | tcgaexp | gene=LOC100133331, entrez=100133331, pos=chr1:322037-180753553(-), B=268, L=328, M=271, H=305 | 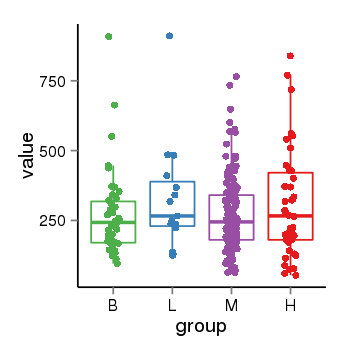 |