DMR 36843 chr1:116932301-116932450 (150bp)
| DMR Stats | |
|---|---|
| Position | chr1:116932301-116932450 (View on UCSC) |
| Width | 150bp |
| Genomic Context | exon |
| Nearest Genes | ATP1A1 (0bp away) |
| ANODEV p-value | 0.000444141261223 |
| Frequencies | Benign: 0.0 (0.0%), Low: 0.0 (0.0%), High: 8.0 (88.89 %) |
| Frequent? |
Region Count Boxplot

Region Overview

Gene Overlaps
| Dmrid | Gene Symbol | Gene Id | Isoform Id | Isoform Chr | Isoform Start | Isoform End | Isoform Strand | Overlap Bp | Query Overlap Per | Isoform Overlap Per | Noncoding | Promoter Per | Exonintron Per | End Per |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 36843 | ATP1A1 | 1388 | uc001ege.3 | chr1 | 116915795 | 116947396 | + | 150 | 100.0 | 1.38 | 0 | 0.0 | E1 (0), I1 (0), E2 (0), I2 (0), E3 (0), I3 (0), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (19.33), I8 (81.33), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0), I16 (0), E17 (0), I17 (0), E18 (0), I18 (0), E19 (0), I19 (0), E20 (0), I20 (0), E21 (0), I21 (0), E22 (0), I22 (0), E23 (0) | 0.0 |
| 36843 | ATP1A1 | 1388 | uc010owv.1 | chr1 | 116915004 | 116946597 | + | 150 | 100.0 | 21.0 | 0 | 0.0 | E1 (0), I1 (0), E2 (0), I2 (0), E3 (0), I3 (0), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (19.33), I8 (81.33), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0), I16 (0), E17 (0), I17 (0), E18 (0), I18 (0), E19 (0), I19 (0), E20 (0), I20 (0), E21 (0), I21 (0), E22 (0) | 0.0 |
| 36843 | ATP1A1 | 1388 | uc010oww.2 | chr1 | 116916489 | 116947396 | + | 150 | 100.0 | 2.71 | 0 | 0.0 | E1 (0), I1 (0), E2 (0), I2 (0), E3 (0), I3 (0), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (19.33), I8 (81.33), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0), I16 (0), E17 (0), I17 (0), E18 (0), I18 (0), E19 (0), I19 (0), E20 (0), I20 (0), E21 (0), I21 (0), E22 (0), I22 (0), E23 (0) | 0.0 |
| 36843 | ATP1A1 | 1388 | uc010owx.2 | chr1 | 116925992 | 116947396 | + | 150 | 100.0 | 15.58 | 0 | 0.0 | E1 (0), I1 (0), E2 (0), I2 (0), E3 (0), I3 (0), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (19.33), I8 (81.33), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0), I16 (0), E17 (0), I17 (0), E18 (0), I18 (0), E19 (0), I19 (0), E20 (0), I20 (0), E21 (0), I21 (0), E22 (0), I22 (0), E23 (0) | 0.0 |
- 4 geness
Feature Overlaps
| Dmrid | Feature Chr | Feature Start | Feature End | Set | Name | Fields |
|---|---|---|---|---|---|---|
| 36843 | chr1 | 116932154 | 116932353 | wgEncodeRegTfbsClusteredV3 | CTCF | score:226, expCount:1, expNums:627, expScores:226, srow:228386 |
| 36843 | chr1 | 116932326 | 116932601 | wgEncodeRegTfbsClusteredV3 | USF2 | score:203, expCount:1, expNums:319, expScores:203, srow:228387 |
| 36843 | chr1 | 116932289 | 116932306 | tfbsConsSites | V$RFX1_02 | score:813, zScore:1.68, srow:278050 |
| 36843 | chr1 | 116932328 | 116932337 | tfbsConsSites | V$NCX_01 | score:903, zScore:2.47, srow:278051 |
| 36843 | chr1 | 116932300 | 116932304 | phastConsElements100way | lod=72 | score:417, srow:485130 |
| 36843 | chr1 | 116932306 | 116932310 | phastConsElements100way | lod=84 | score:432, srow:485131 |
| 36843 | chr1 | 116932313 | 116932322 | phastConsElements100way | lod=114 | score:462, srow:485132 |
| 36843 | chr1 | 116932324 | 116932338 | phastConsElements100way | lod=165 | score:499, srow:485133 |
- 8 featuress
Omics Overlaps
| Dmrid | Omic Set | Data | Plot |
|---|---|---|---|
| 36843 | cellmeth_recounts | PrEC: 6, LNCaP: 3, DU145: 0 |  |
| 36843 | cellexp | id=ENSG00000163399, name=ATP1A1, PrEC=38127, str=46875, LNCaP=24742, str=25775, DU145=21311, str=19351 |  |
| 36843 | tcgaexp | gene=ATP1A1, entrez=476, pos=chr1:116915004-116947396(+), B=54793, L=44752, M=47215, H=42592 |  |
| 36843 | tcgaexp | gene=LOC100133331, entrez=100133331, pos=chr1:322037-180753553(-), B=268, L=328, M=271, H=305 | 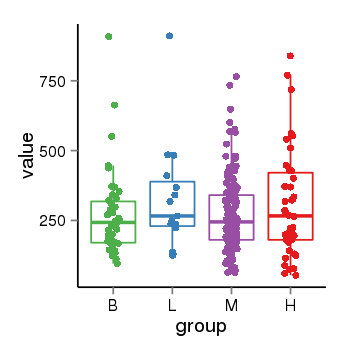 |
| 36843 | pubmed | gene=ATP1A1, G=242, GP=0, GC=23, GM=8, GPM=0, GCM=0 |  |