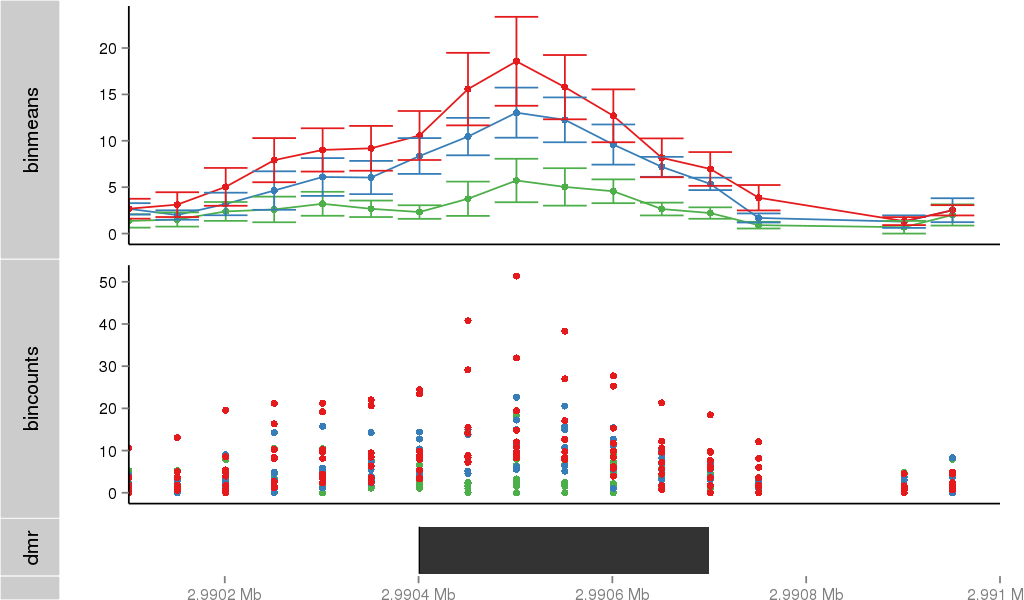
DMR 24905 chr1:2990401-2990700 (300bp)
| DMR Stats | |
|---|---|
| Position | chr1:2990401-2990700 (View on UCSC) |
| Width | 300bp |
| Genomic Context | intron |
| Nearest Genes | PRDM16 (0bp away) |
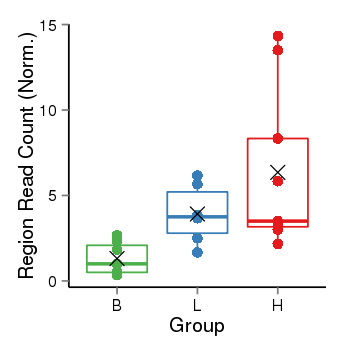
| ANODEV p-value | 0.0124612180468 |
| Frequencies | Benign: 0.0 (0.0%), Low: 4.0 (66.67%), High: 7.0 (77.78 %) |
| Frequent? |
Region Count Boxplot
Region Overview
Gene Overlaps
| Dmrid | Gene Symbol | Gene Id | Isoform Id | Isoform Chr | Isoform Start | Isoform End | Isoform Strand | Overlap Bp | Query Overlap Per | Isoform Overlap Per | Noncoding | Promoter Per | Exonintron Per | End Per |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 24905 | PRDM16 | 117 | uc001akc.3 | chr1 | 2985742 | 3355185 | + | 300 | 100.0 | 0.33 | 0 | 0.0 | E1 (0), I1 (100), E2 (0), I2 (0), E3 (0), I3 (0), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (0), I8 (0), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0), I16 (0), E17 (0) | 0.0 |
| 24905 | PRDM16 | 117 | uc001ake.3 | chr1 | 2985742 | 3355185 | + | 300 | 100.0 | 1.0 | 0 | 0.0 | E1 (0), I1 (100), E2 (0), I2 (0), E3 (0), I3 (0), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (0), I8 (0), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0), I16 (0), E17 (0) | 0.0 |
| 24905 | PRDM16 | 117 | uc001akf.3 | chr1 | 2985742 | 3355185 | + | 300 | 100.0 | 0.33 | 0 | 0.0 | E1 (0), I1 (100), E2 (0), I2 (0), E3 (0), I3 (0), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (0), I8 (0), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0), I16 (0), E17 (0) | 0.0 |
| 24905 | PRDM16 | 117 | uc009vlh.3 | chr1 | 2985742 | 3355185 | + | 300 | 100.0 | 0.33 | 0 | 0.0 | E1 (0), I1 (100), E2 (0), I2 (0), E3 (0), I3 (0), E4 (0), I4 (0), E5 (0), I5 (0), E6 (0), I6 (0), E7 (0), I7 (0), E8 (0), I8 (0), E9 (0), I9 (0), E10 (0), I10 (0), E11 (0), I11 (0), E12 (0), I12 (0), E13 (0), I13 (0), E14 (0), I14 (0), E15 (0), I15 (0), E16 (0), I16 (0), E17 (0) | 0.0 |
- 4 geness
Feature Overlaps
| Dmrid | Feature Chr | Feature Start | Feature End | Set | Name | Fields |
|---|---|---|---|---|---|---|
| 24905 | chr1 | 2990586 | 2991670 | wgEncodeRegDnaseClusteredV2 | 43 | score:1000, srow:2136 |
| 24905 | chr1 | 2988901 | 2990875 | wgEncodeRegTfbsClusteredV3 | EZH2 | score:653, expCount:3, expNums:6,21,36, expScores:294,653,209, srow:8633 |
| 24905 | chr1 | 2989842 | 2990878 | wgEncodeRegTfbsClusteredV3 | SUZ12 | score:260, expCount:2, expNums:358,578, expScores:95,205, srow:8636 |
| 24905 | chr1 | 2990031 | 2990718 | cpgIsland | CpG: 82 | length:688, cpgNum:82, gcNum:509, perCpg:23.8, perGc:74, obsExp:0.87, srow:236 |
- 4 featuress
Omics Overlaps
| Dmrid | Omic Set | Data | Plot |
|---|---|---|---|
| 24905 | cellmeth_recounts | PrEC: 11, LNCaP: 179, DU145: 3 | 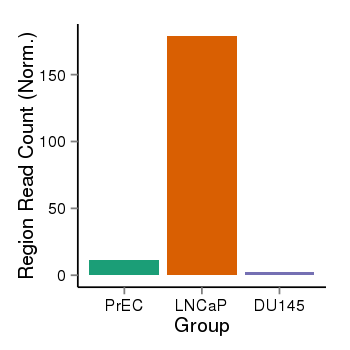 |
| 24905 | cellmeth_diffreps_PrECvsLNCaP | A=16, B=233, Length=600, Event=Up, log2FC=3.86, padj=0 | 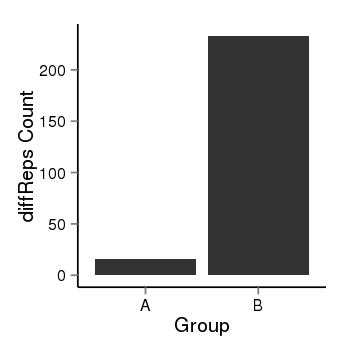 |
| 24905 | cellmeth_diffreps_LNCaPvsDU145 | A=249.09, B=7.48, Length=660, Event=Down, log2FC=-5.06, padj=0 | 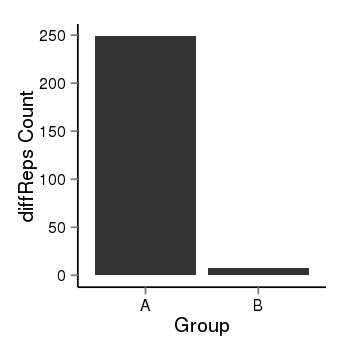 |
| 24905 | cellexp | id=ENSG00000142611, name=PRDM16, PrEC=8, str=18, LNCaP=18, str=10, DU145=49, str=42 | 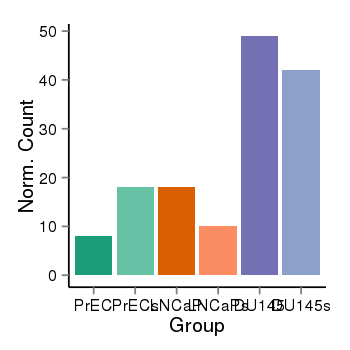 |
| 24905 | tcgameth | site:cg17001566, B=0.26, L=0.58, H=0.54 | 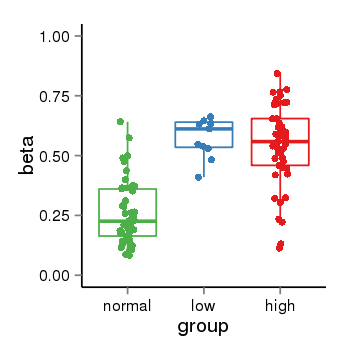 |
| 24905 | tcgameth | site:cg22726349, B=0.47, L=0.63, H=0.58 | 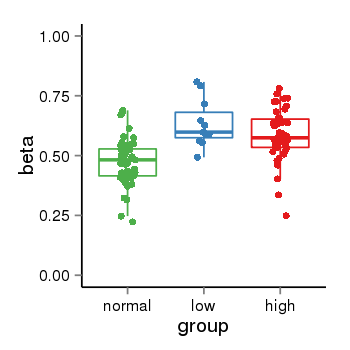 |
| 24905 | tcgaexp | gene=SRSF10, entrez=10772, pos=chr1:36273-24306953(-), B=3487, L=3388, M=3432, H=4019 | 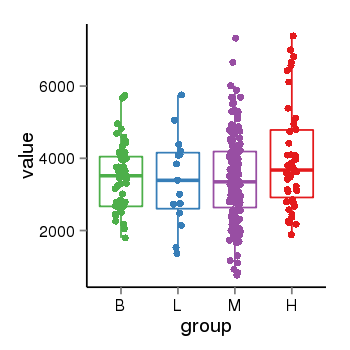 |
| 24905 | tcgaexp | gene=PRDM16, entrez=63976, pos=chr1:2985742-3355185(+), B=306, L=40, M=53, H=56 | 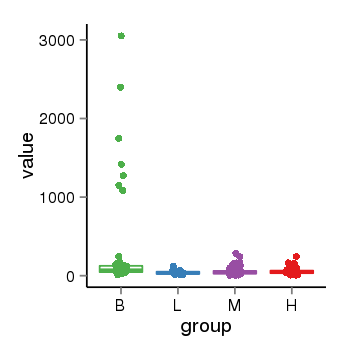 |
| 24905 | tcgaexp | gene=LOC100133331, entrez=100133331, pos=chr1:322037-180753553(-), B=268, L=328, M=271, H=305 | 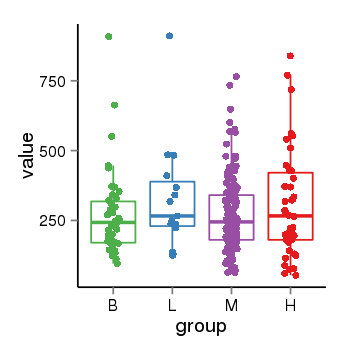 |